ping @MatthiasHerrmann @mtw
Closed martin-raden closed 8 months ago
ping @MatthiasHerrmann @mtw
der lineplot sieht gut aus! wie von @martin-raden erwähnt wäre es schön, ein klassifizierung im lineplot zu sehen. am besten würde sich hier die ecologic group (in deiner parameter_table wäre das die Spalte "type") eignen. wir kennen für jede dieser sequenzen die konservierten RNA strukturelemente, bzw können wir die genaue position innerhalb der 3 bzw 5utr mit hilfe von covarianzmodellen leicht bestimmen. in der literatur wird manchmal erwähnt dass die cyclisation sequenzen oft benachbart zu bestimmten RNA strukturelementen gefunden wurden (zumindest bei den paar beispielen die genauer analysiert wurden). in weiterer folge wäre es daher auch gut, diese als farblich gekennzeichnete blöcke in den lineplot mit aufzunehmen. lass und das im nächsten call genauer besprechen.
der lineplot sieht gut aus! wie von @martin-raden erwähnt wäre es schön, ein klassifizierung im lineplot zu sehen. am besten würde sich hier die ecologic group (in deiner parameter_table wäre das die Spalte "type") eignen. wir kennen für jede dieser sequenzen die konservierten RNA strukturelemente, bzw können wir die genaue position innerhalb der 3 bzw 5utr mit hilfe von covarianzmodellen leicht bestimmen. in der literatur wird manchmal erwähnt dass die cyclisation sequenzen oft benachbart zu bestimmten RNA strukturelementen gefunden wurden (zumindest bei den paar beispielen die genauer analysiert wurden). in weiterer folge wäre es daher auch gut, diese als farblich gekennzeichnete blöcke in den lineplot mit aufzunehmen. lass und das im nächsten call genauer besprechen.
siehe https://www.biorxiv.org/content/10.1101/2022.08.18.504478v2.full.pdf seite 43, da sind so elemente farblich markiert
frage: sind interactions im 5'UTR korreliert mit stemloopA auflösung, siehe https://michaelwolfinger.com/files/papers/Harima-2021.pdf figure 5a
check for parallel formbare multi-site interactions
hab gerade den neuen lineplot angeschaut: sehr schick! scheinbar liegen die 3'UTR interactions häufig in relativ gleichem abstand zum genomende..
Danke!
hab gerade mal meine R skills erprobt und im R_viz branch was gebastelt, was ich meine:
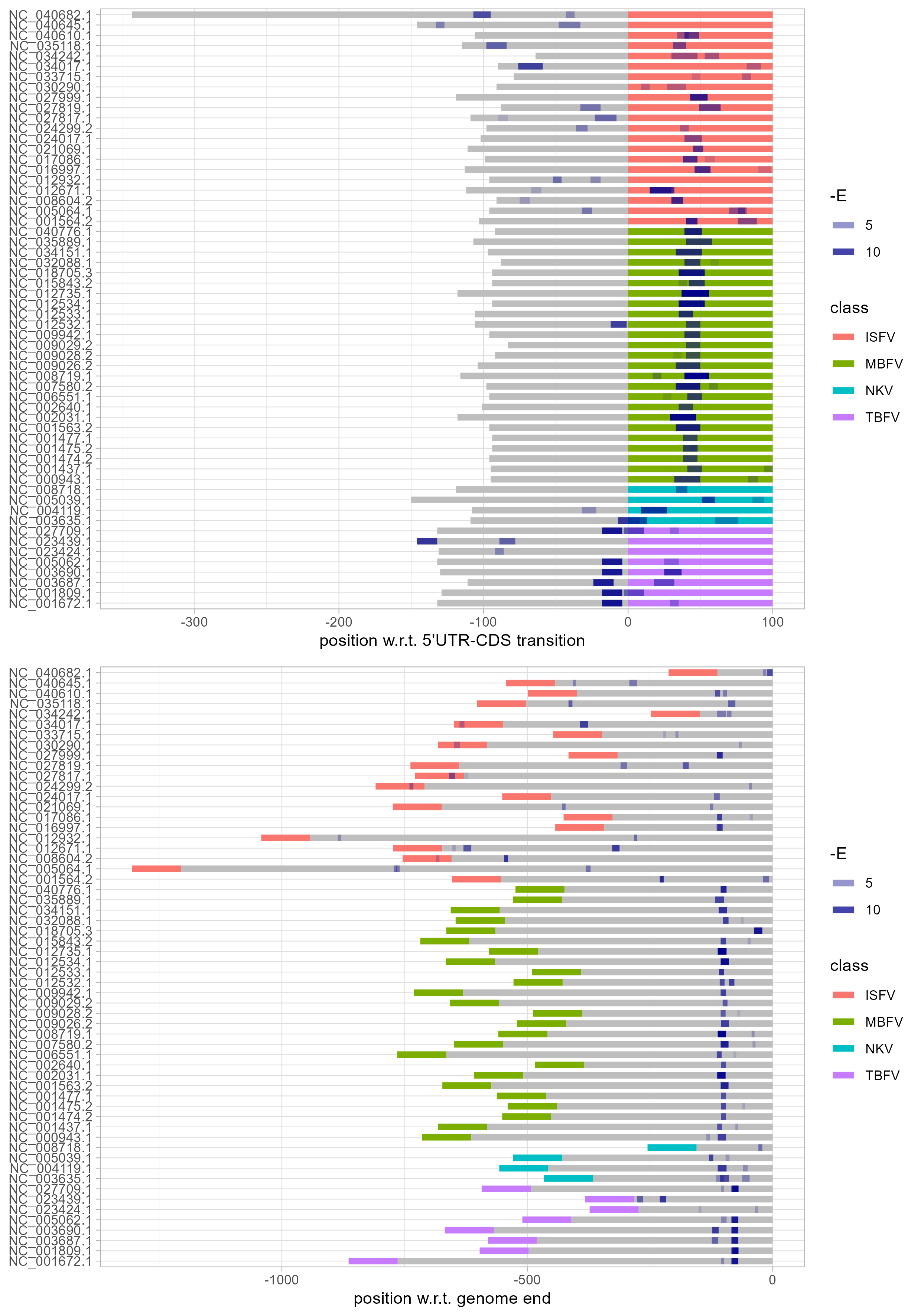
glaub mit den Änderungen, die ich per Email geschickt hatte, sieht man da einiges..
hab gerade den neuen lineplot angeschaut: sehr schick! scheinbar liegen die 3'UTR interactions häufig in relativ gleichem abstand zum genomende..
* [ ] könntest du ggf. einen dritten lineplot noch drunter setzen, der bzgl genomende "aligniert ist"? dazu müsstest du von alle koordinaten einfach die UTR länge abziehen, dann sollte das genomende die 0 haben und alle annotations entsprechend verschoben werden...Danke!
update: keinen dritten plot machen, sondern den 3'UTR plot bzgl genomende anpassen und gut... Danke!
Ich habe es jetzt vorerst als 3. Plot gemacht. Ich meine, das ist sogar genau das, was ich am Anfang hatte oder? Zumindest für das 3' Ende
Ich habe es jetzt vorerst als 3. Plot gemacht. Ich meine, das ist sogar genau das, was ich am Anfang hatte oder? Zumindest für das 3' Ende
passt, super so! Danke!
um das verschieben obsolete zu machen, hatte ich vorgeschlagen, dass du schon im intarna call die "idxpos0" positions entsprechend setzt, dann sind ist interaction position information nämlich schon bzgl. selbiger.. aber kann auch als postprocessing fürs visualisieren reingepackt werden
[x] ich würd die gruppen im lineplot gern sehen.. dazu ggf. die CDS (oder den UTR) entsprechend einfärben und eine farblegende neben den plot packen.
[x] der lineplot würde sich mächtig gut eignen auch alternative interaktionsstellen zu visualisieren.
dazu müsste man intarna am besten 2mal aufrufen, um non-overlapping interactions in der einen oder der anderen sequenz zu erlauben/verbieten
die ergebnisse könnte man dann entsprechend noch eintragen, ggf. mit colorscale basierend auf der entsprechenden energie
damit könnte man dann sehen, ob ggf. second best interactions in die konservierten locations passen...